Este artigo é sobre o haplogrupo do mtDNA humano. Para o haplogrupo Y-DNA humano, consulte
Haplogrupo I-M170 .
O haplogrupo I é um haplogrupo de DNA mitocondrial humano (mtDNA). Acredita-se que tenha se originado há cerca de 21.000 anos, durante o período do Último Máximo Glacial (LGM) na Ásia Ocidental (( Olivieri 2013 ); Terreros 2011 ; Fernandes 2012 ). O haplogrupo é incomum porque agora está amplamente distribuído geograficamente, mas é comum apenas em algumas pequenas áreas da África Oriental , Ásia Ocidental e Europa . É especialmente comum entre os povos El Molo e Rendille do Quênia, várias regiões do Irã , o povo Lemko da Eslováquia, Polônia e Ucrânia, a ilha de Krk na Croácia, o departamento de Finistère na França e algumas partes da Escócia e Irlanda .
Origem
O haplogrupo I é um descendente ( subclado ) do haplogrupo N1a1b e irmão do haplogrupo N1a1b1 ( Olivieri 2013 ). Acredita-se que tenha surgido em algum lugar da Ásia Ocidental entre 17.263 e 24.451 anos antes do presente (BP) ( Behar 2012b ), com idade de coalescência de 20,1 mil anos atrás ( Olivieri 2013 ). Foi sugerido que sua origem pode ser no Irã ou mais geralmente no Oriente Próximo ( Terreros 2011 ). Ele divergiu para pelo menos sete clados distintos, ou seja, ramos I1-I7, datados entre 16-6,8 mil anos ( Olivieri 2013 ). A hipótese sobre sua origem no Oriente Próximo é baseada no fato de que todos os clados do haplogrupo I, especialmente aqueles do período Glacial Superior (I1, I4, I5 e I6), incluem mitogenomas do Oriente Próximo ( Olivieri 2013 ). As estimativas de idade e dispersão de alguns subclados (I1, I2'3, I5) são semelhantes às dos subclados principais dos haplogrupos J e T do mtDNA , indicando possível dispersão do haplogrupo I na Europa durante o período glacial tardio (c. 18 –12 kya) e período pós-glacial (c. 10–11 kya), vários milênios antes do período Neolítico europeu. Alguns subclados (I1a1, I2, I1c1, I3) mostram sinais da difusão neolítica da agricultura e pastoralismo na Europa ( Olivieri 2013 ).
É digno de nota que, com exceção de seu vizinho do norte, o Azerbaijão, o Irã é a única população em que o haplogrupo I exibe níveis polimórficos. Além disso, um gráfico de contorno com base na distribuição filogeográfica regional do haplogrupo I exibe clines de frequência consistentes com um berço iraniano ... Além disso, quando comparado com outras populações da região, as do Levante (Iraque, Síria e Palestina) e os A Península Arábica (Omã e Emirados Árabes Unidos) exibe proporções significativamente mais baixas de indivíduos I ... este haplogrupo foi detectado em grupos europeus (Krk, uma pequena ilha na costa da Croácia (11,3%), e Lemko, um isolado das terras altas dos Cárpatos (11,3%)) em frequências comparáveis às observadas na população do norte do Irã. No entanto, as frequências mais altas do haplogrupo dentro da Europa são encontradas em isolados geográficos e são provavelmente o resultado de efeitos fundadores e / ou deriva ... é plausível que os altos níveis de haplogrupo I presentes no Irã possam ser o resultado de uma o enriquecimento por ação da deriva genética ou pode sinalizar proximidade geográfica com o local de origem.
- Terreros 2011
Uma visão semelhante coloca mais ênfase na região do Golfo Pérsico no Oriente Próximo ( Fernandes 2012 ).
O Haplogrupo I ... data de ∼25 ka atrás e é geralmente mais frequente na Europa ..., mas os fatos de que tem um pico de frequência na região do Golfo e que seus maiores valores de diversidade estão no Golfo, Anatólia e sudeste A Europa sugere que sua origem é mais provavelmente no Oriente Próximo e / ou Arábia ...
Distribuição
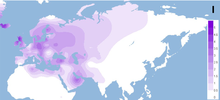
Freqüências projetadas do haplogrupo I. do mtDNA
O haplogrupo I é encontrado em frequências moderadas a baixas na África Oriental , Europa , Ásia Ocidental e Sul da Ásia ( Fernandes 2012 ). Além dos sete clados confirmados, o raro clado I * basal / parafilético foi observado em três indivíduos; dois da Somália e um do Irã ( Olivieri 2013 ).
África
As frequências mais altas do haplogrupo mitocondrial que observei até agora aparecem no El Molo de língua cushítica (23%) e Rendille (> 17%) no norte do Quênia ( Castrì 2008 ). O clado também é encontrado em frequências comparáveis entre os Soqotri (~ 22%).
|
População
|
Localização
|
Família da Língua
|
N
|
Frequência
|
Fonte
|
| Amhara |
Etiópia |
Afro-Asiático> Semita |
1/120 |
0,83% |
Kivisild 2004
|
| Egípcios |
Egito |
Afro-Asiático> Semita |
2/34 |
5,9% |
Stevanovitch 2004
|
| Beta Israel |
Etiópia |
Afro-Asiático> Cushitic |
0/29 |
0,00% |
Behar 2008a
|
| Dawro Konta |
Etiópia |
Afro-Asiático> Omótico |
0/137 |
0,00% |
Castrì 2008 e Boattini 2013
|
| Etiópia |
Etiópia |
Indeterminado |
0/77 |
0,00% |
Soares 2011
|
| Judeus etíopes |
Etiópia |
Afro-Asiático> Cushitic |
0/41 |
0,00% |
Não 2011
|
| Gurage |
Etiópia |
Afro-Asiático> Semita |
21/01 |
4,76% |
Kivisild 2004
|
| Hamer |
Etiópia |
Afro-Asiático> Omótico |
0/11 |
0,00% |
Castrì 2008 e Boattini 2013
|
| Ongota |
Etiópia |
Afro-Asiático> Cushitic |
0/19 |
0,00% |
Castrì 2008 e Boattini 2013
|
| Oromo |
Etiópia |
Afro-Asiático> Cushitic |
0/33 |
0,00% |
Kivisild 2004
|
| Tigrai |
Etiópia |
Afro-Asiático> Semita |
0/44 |
0,00% |
Kivisild 2004
|
| Daasanach |
Quênia |
Afro-Asiático> Cushitic |
0/49 |
0,00% |
Poloni 2009
|
| Elmolo |
Quênia |
Afro-Asiático> Cushitic |
12/52 |
23,08% |
Castrì 2008 e Boattini 2013
|
| Luo |
Quênia |
Nilo-saariano |
0/49 |
0,00% |
Castrì 2008 e Boattini 2013
|
| Maasai |
Quênia |
Nilo-saariano |
0/81 |
0,00% |
Castrì 2008 e Boattini 2013
|
| Nairobi |
Quênia |
Niger-Congo |
0/100 |
0,00% |
Brandstatter 2004
|
| Nyangatom |
Quênia |
Nilo-saariano |
1/112 |
0,89% |
Poloni 2009
|
| Rendille |
Quênia |
Afro-Asiático> Cushitic |
17/03 |
17,65% |
Castrì 2008 e Boattini 2013
|
| Samburu |
Quênia |
Nilo-saariano |
3/35 |
8,57% |
Castrì 2008 e Boattini 2013
|
| Turkana |
Quênia |
Nilo-saariano |
0/51 |
0,00% |
Castrì 2008 e Boattini 2013
|
| Hutu |
Ruanda |
Niger-Congo |
0/42 |
0,00% |
Castrì 2009
|
| Dinka |
Sudão |
Nilo-saariano |
0/46 |
0,00% |
Krings 1999
|
| Sudão |
Sudão |
Indeterminado |
0/102 |
0,00% |
Soares 2011
|
| Burunge |
Tanzânia |
Afro-Asiático> Cushitic |
1/38 |
2,63% |
Tishkoff 2007
|
| Datoga |
Tanzânia |
Nilo-saariano |
0/57 |
0,00% |
Tishkoff 2007 e Knight 2003
|
| Iraquiano |
Tanzânia |
Afro-Asiático> Cushitic |
0/12 |
0,00% |
Knight 2003
|
| Sukuma |
Tanzânia |
Niger-Congo |
0/32 |
0,00% |
Tishkoff 2007 e Knight 2003
|
| Turu |
Tanzânia |
Niger-Congo |
0/29 |
0,00% |
Tishkoff 2007
|
| Iemenita |
Iémen |
Afro-Asiático> Semita |
0/114 |
0,00% |
Kivisild 2004
|
Ásia
O Haplogrupo I está presente na Ásia Ocidental e na Ásia Central, e também é encontrado em frequências de rastreamento no Sul da Ásia. Sua área de maior frequência talvez esteja no norte do Irã (9,7%). Terreros 2011 observa que também tem alta diversidade lá e reitera estudos anteriores que sugeriram que este pode ser o seu local de origem. Encontrado na população Svan da Geórgia (Cáucaso) I * 4,2%. "Polimorfismos de sequência da região de controle do mtDNA em um isolado humano: os georgianos de Swanetia." Alfonso-Sánchez MA1, Martínez-Bouzas C, Castro A, Peña JA, Fernández -Fernández I, Herrera RJ, de Pancorbo MM. A tabela abaixo mostra algumas das populações onde foi detectado.
|
População
|
Família da Língua
|
N
|
Frequência
|
Fonte
|
| Baluch |
Indo-europeu |
0/39 |
0,00% |
Quintana-Murci 2004
|
| Brahui |
Dravidiano |
0/38 |
0,00% |
Quintana-Murci 2004
|
| Cáucaso (Geórgia) * |
Kartveliano |
1/58 |
1,80% |
Quintana-Murci 2004
|
| Drusa |
- |
11/311 |
3,54% |
Shlush 2008
|
| Gilaki |
Indo-europeu |
0/37 |
0,00% |
Quintana-Murci 2004
|
| Guzerate |
Indo-europeu |
0/34 |
0,00% |
Quintana-Murci 2004
|
| Hazara |
Indo-europeu |
0/23 |
0,00% |
Quintana-Murci 2004
|
| Hunza Burusho |
Isolar |
2/44 |
4,50% |
Quintana-Murci 2004
|
| Índia |
- |
25/0844 |
0,30% |
Metspalu 2004
|
| Irã (Norte) |
- |
31/03 |
9,70% |
Terreros 2011
|
| Irã (sul) |
- |
2/117 |
1,70% |
Terreros 2011
|
| Kalash |
Indo-europeu |
0/44 |
0,00% |
Quintana-Murci 2004
|
| Curdo (oeste do Irã) |
Indo-europeu |
1/20 |
5,00% |
Quintana-Murci 2004
|
| Curdo (Turcomenistão) |
Indo-europeu |
1/32 |
3,10% |
Quintana-Murci 2004
|
| Lur |
Indo-europeu |
0/17 |
0,00% |
Quintana-Murci 2004
|
| Makrani |
Indo-europeu |
0/33 |
0,00% |
Quintana-Murci 2004
|
| Mazandariano |
Indo-europeu |
21/01 |
4,80% |
Quintana-Murci 2004
|
| paquistanês |
Indo-europeu |
0/100 |
0,00% |
Quintana-Murci 2004
|
| Paquistão |
- |
1/145 |
0,69% |
Metspalu 2004
|
| Parsi |
Indo-europeu |
0/44 |
0,00% |
Quintana-Murci 2004
|
| Pathan |
Indo-europeu |
1/44 |
2,30% |
Quintana-Murci 2004
|
| persa |
Indo-europeu |
1/42 |
2,40% |
Quintana-Murci 2004
|
| Shugnan |
Indo-europeu |
1/44 |
2,30% |
Quintana-Murci 2004
|
| Sindi |
Indo-europeu |
23/01 |
8,70% |
Quintana-Murci 2004
|
| Turco (Azerbaijão) |
Turco |
2/40 |
5,00% |
Quintana-Murci 2004
|
| Turco (Anatólia) * |
Turco |
1/50 |
2,00% |
Quintana-Murci 2004
|
| Turcomano |
Turco |
0/41 |
0,00% |
Quintana-Murci 2004
|
| Uzbeque |
Turco |
0/42 |
0,00% |
Quintana-Murci 2004
|
Europa
Europa Ocidental
Na Europa Ocidental, o haplogrupo I é mais comum no noroeste da Europa (Noruega, Ilha de Skye e Ilhas Britânicas). A frequência nessas áreas está entre 2 e 5 por cento. Sua maior frequência é na Bretanha, França, onde representa mais de 9% da população de Finistère . É incomum e às vezes ausente em outras partes da Europa Ocidental (Península Ibérica, Sudoeste da França e partes da Itália).
|
População
|
Língua
|
N
|
Frequência
|
Fonte
|
| Áustria / Suíça |
- |
4/187 |
2,14% |
Helgason 2001
|
| Basco (zona de mistura) |
Basco / Labourdin côtier-haut navarrais |
0/56 |
0,00% |
Martınez-Cruz 2012
|
| Basco (árabe) |
Basco / ocidental |
0/55 |
0,00% |
Martınez-Cruz 2012
|
| Basco (Bizkaia) |
Basco / Biscaia |
1/59 |
1,69% |
Martınez-Cruz 2012
|
| Basco (Navarra Central / Ocidental) |
Basco / Haut-navarrais méridional |
2/63 |
3,17% |
Martınez-Cruz 2012
|
| Basco (Gipuskoa) |
Basco / gipuzkoan |
0/57 |
0,00% |
Martınez-Cruz 2012
|
| Basco (Navarra Labourdin) |
Basco / bas-navarrais |
0/68 |
0,00% |
Martınez-Cruz 2012
|
| Basco (Norte / Oeste de Navarra) |
Setentrional basco / haut-navarrais |
0/51 |
0,00% |
Martınez-Cruz 2012
|
| Basco (Roncal) |
Basco / roncalais-salazarais |
0/55 |
0,00% |
Martınez-Cruz 2012
|
| Basco (soule) |
Basco / souletin |
0/62 |
0,00% |
Martınez-Cruz 2012
|
| Basco (sul / oeste de Gipuskoa) |
Basco / Biscaia |
0/64 |
0,00% |
Martınez-Cruz 2012
|
| Béarn |
francês |
0/51 |
0,00% |
Martınez-Cruz 2012
|
| Bigorre |
francês |
0/44 |
0,00% |
Martınez-Cruz 2012
|
| Burgos |
espanhol |
0/25 |
0,00% |
Martınez-Cruz 2012
|
| Cantabria |
espanhol |
0/18 |
0,00% |
Martınez-Cruz 2012
|
| Chalosse |
francês |
0/58 |
0,00% |
Martınez-Cruz 2012
|
| Dinamarca |
- |
6/105 |
5,71% |
Mikkelsen 2010
|
| Inglaterra / País de Gales |
- |
12/429 |
3,03% |
Helgason 2001
|
| Finlândia |
- |
1/49 |
2,04% |
Torroni 1996
|
| Finlândia / Estônia |
- |
5/202 |
2,48% |
Helgason 2001
|
| França (Finistère) |
- |
22/02 |
9,10% |
Dubut 2003
|
| França (Morbihan) |
- |
0/40 |
0,00% |
Dubut 2003
|
| França (Normandia) |
- |
0/39 |
0,00% |
Dubut 2003
|
| França (Périgord-Limousin) |
- |
2/72 |
2,80% |
Dubut 2003
|
| França (Var) |
- |
2/37 |
5,40% |
Dubut 2003
|
| França / Itália |
- |
2/248 |
0,81% |
Helgason 2001
|
| Alemanha |
- |
12/527 |
2,28% |
Helgason 2001
|
| Islândia |
- |
21/467 |
4,71% |
Helgason 2001
|
| Irlanda |
- |
3/128 |
2,34% |
Helgason 2001
|
| Itália (Toscana) |
- |
2/48 |
4,20% |
Torroni 1996
|
| La Rioja |
espanhol |
1/51 |
1,96% |
Martınez-Cruz 2012
|
| Aragão do Norte |
espanhol |
0/26 |
0,00% |
Martınez-Cruz 2012
|
| Orkney |
- |
5/152 |
3,29% |
Helgason 2001
|
| Saami |
- |
0/176 |
0,00% |
Helgason 2001
|
| Escandinávia |
- |
12/645 |
1,86% |
Helgason 2001
|
| Escócia |
- |
39/891 |
4,38% |
Helgason 2001
|
| Espanha / Portugal |
- |
2/352 |
0,57% |
Helgason 2001
|
| Suécia |
- |
0/37 |
0,00% |
Torroni 1996
|
| Bizkaia Ocidental |
espanhol |
0/18 |
0,00% |
Martınez-Cruz 2012
|
| Ilhas Ocidentais / Ilha de Skye |
- |
15/246 |
6,50% |
Helgason 2001
|
Europa Oriental
Na Europa Oriental, a frequência do haplogrupo I é geralmente menor do que na Europa Ocidental (1 a 3 por cento), mas sua frequência é mais consistente entre populações com menos locais de altos ou baixos extremos. Existem duas exceções notáveis. Nikitin 2009 descobriu que os Lemkos (um sub ou co-grupo étnico de Rusyns ) nas montanhas dos Cárpatos têm a "maior frequência de haplogrupo I (11,3%) na Europa, idêntica à da população da Ilha de Krk (Croácia) no Mar Adriático".
| População
|
N
|
Frequência
|
Fonte
|
| Boyko |
0/20 |
0,00% |
Nikitin 2009
|
| Hutsul |
0/38 |
0,00% |
Nikitin 2009
|
| Lemko |
6/53 |
11,32% |
Nikitin 2009
|
| Bielo-russos |
2/92 |
2,17% |
Belyaeva 2003
|
| Rússia (europeu) |
3/215 |
1,40% |
Helgason 2001
|
| Romenos (Constanta) |
59 |
0,00% |
Bosch 2006
|
| Romenos (Ploiesti) |
46 |
2,17% |
Bosch 2006
|
| Rússia |
1/50 |
2,0% |
Malyarchuk 2001
|
| Ucrânia |
0/18 |
0,00% |
Malyarchuk 2001
|
| Croácia (continente) |
4/277 |
1,44% |
Pericić 2005
|
| Croácia (Krk) |
15/133 |
11,28% |
Cvjetan 2004
|
| Croácia (Brac) |
1/105 |
0,95% |
Cvjetan 2004
|
| Croácia (Hvar) |
2/108 |
1,9% |
Cvjetan 2004
|
| Croácia (Korcula) |
1/98 |
1% |
Cvjetan 2004
|
| Herzegovinianos |
1/130 |
0,8% |
Cvjetan 2004
|
| Bósnios |
6/247 |
2,4% |
Cvjetan 2004
|
| Sérvios |
4/117 |
3,4% |
Cvjetan 2004
|
| Macedônios |
2/146 |
1,4% |
Cvjetan 2004
|
| Romani da Macedônia |
7/153 |
4,6% |
Cvjetan 2004
|
| Eslovenos |
2/104 |
1,92% |
Malyarchuk 2003
|
| Bósnios |
4/144 |
2,78% |
Malyarchuk 2003
|
| Poloneses |
8/436 |
1,83% |
Malyarchuk 2003
|
| Cáucaso (Geórgia) * |
1/58 |
1,80% |
Quintana-Murci 2004
|
| Russos |
5/201 |
2,49% |
Malyarchuk 2003
|
| Bulgária / Turquia |
2/102 |
1,96% |
Helgason 2001
|
Amostras históricas e pré-históricas
O haplogrupo I estava ausente até recentemente nas amostras europeias antigas encontradas em túmulos do Paleolítico e do Mesolítico. Em 2017, em um local na ilha italiana da Sardenha foi encontrada uma amostra com o subclado I3 datado de 9124-7851 aC ( Modi 2017 ), enquanto no Oriente Próximo, no Levante foi encontrada uma amostra com o subclado ainda não definido datado 8.850-8.750 aC, enquanto no Irã foi encontrada uma amostra mais jovem com o subclado I1c datado de 3972-3800 aC ( Lazaridis 2016 ). Na Espanha neolítica (c. 6090-5960 aC em Paternanbidea , Navarra ) foi encontrada uma amostra com subclado ainda não definido ( Olivieri 2013 ). O Haplogrupo I mostra uma forte ligação com as migrações indo-europeias ; especialmente seus subclades I1, I1a1 e I3A, que foram encontrados em Poltavka e Srubnaya culturas na Rússia (Mathieson 2015), entre antigos citas (Der Sarkissian 2011), e em Corded Ware e Cultura Unetice enterros em Saxônia ( Brandt 2013 ) .I3A também foi encontrado na Cultura Unetice em Lubingine, Alemanha 2.200 aC a 1.800 aC, artigo de cortesia na Wikipédia sobre cultura da Unetice de 2 esqueletos que foram testados com DNA. O haplogrupo I (com subclados indeterminados) também foi observado em frequências significativas em túmulos históricos mais recentes ( Melchior 2008 e Hofreiter 2010 ).
Em 2013, a Nature anunciou a publicação do primeiro estudo genético utilizando sequenciamento de próxima geração para determinar a linhagem ancestral de um indivíduo do Egito Antigo . A pesquisa foi liderada por Carsten Pusch, da Universidade de Tübingen, na Alemanha, e Rabab Khairat, que divulgaram suas descobertas no Journal of Applied Genetics . O DNA foi extraído da cabeça de cinco múmias egípcias que estavam alojadas na instituição. Todos os espécimes foram datados entre 806 AC e 124 DC, um período de tempo que corresponde aos períodos dinástico tardio e ptolomaico . Os pesquisadores observaram que um dos indivíduos mumificados provavelmente pertencia ao subclado I2. O haplogrupo I também foi encontrado entre múmias egípcias antigas escavadas no sítio arqueológico Abusir el-Meleq no Oriente Médio, que datam dos períodos pré-ptolomaico / final do Novo Império , ptolomaico e romano .
O haplogrupo I5 também foi observado entre os espécimes no cemitério do continente em Kulubnarti , Sudão , que data do período cristão primitivo (550-800 DC).
Amostras com subclados determinados
|
Cultura
|
País
|
Local
|
Encontro
|
Haplogrupo
|
Fonte
|
| Unetice |
Alemanha |
Esperstedt |
2050-1800 a.C. |
I1 |
Adler 2012; Brandt 2013
|
| Bell Beaker |
Alemanha |
- |
2600-2500 AC |
I1a1 |
Lee 2012; Oliveiri 2013
|
| Unetice |
Alemanha |
Plotzkau 3 |
2200-1550 AC |
I1a1 |
Brandt 2013
|
| Unetice |
Alemanha |
Eulau |
1979-1921 AC |
I1a1 |
Brandt 2013
|
| Srubnaya |
Rússia |
Rozhdestveno I, Samara Steppes, Samara |
1850-1600 AC |
I1a1 |
Mathieson 2015
|
| Seh Gabi |
Irã |
- |
3972-3800 AC |
I1c |
Lazaridis 2016
|
| Cami de Can Grau |
Espanha |
- |
3500-3000 AC |
I1c1 |
Sampietro 2007; Olivieri 2013
|
| Tardio Dinástico-Ptolomaico |
Egito |
- |
806 BC-124 DC |
I2 |
Khairat 2013
|
| Su Carroppu |
Itália |
- |
9124-7851 AC |
I3 |
Modi 2017
|
| cita |
Rússia |
Rostov-on-Don |
500-200 AC |
I3 |
Der Sarkissian 2011
|
| Unetice |
Alemanha |
Benzingerode-Heimburg |
1653-1627 AC |
I3a |
Brandt 2013
|
| Unetice |
Alemanha |
Esperstedt |
2131-1979 AC |
I3a |
Adler 2012; Brandt 2013; Haak 2015; Mathieson 2015
|
| Unetice |
Alemanha |
Esperstedt |
2199-2064 AC |
I3a |
Adler 2012; Brandt 2013; Haak 2015
|
| Poltavka |
Rússia |
Lopatino II, Rio Sok, Samara |
2885-2665 AC |
I3a |
Mathieson 2015
|
| Karasuk |
Rússia |
Sabinka 2 |
1416-1268 AC |
I4a1 |
Allentoft 2015
|
| Minóico |
Grécia |
Ayios Charalambos |
2.400-1700 AC |
I5 |
Hughey 2013
|
| Minóico |
Grécia |
Ayios Charalambos |
2.400-1700 AC |
I5 |
Hughey 2013
|
| Minóico |
Grécia |
Ayios Charalambos |
2.400-1700 AC |
I5 |
Hughey 2013
|
| Nubia Cristã |
Sudão |
Kulubnarti |
550-800 DC |
I5 |
Sirak 2016
|
| Idade do Bronze Final |
Armênia |
Norabak |
1209-1009 AC |
I5c |
Allentoft 2015
|
| Mezhovskava |
Rússia |
Caverna Kapova |
1598-1398 AC |
I5c |
Allentoft 2015
|
Amostras com subclados desconhecidos
| Populações
|
N
|
Frequência
|
Fonte
|
Locais da Idade do Ferro Romana
Bøgebjerggård (AD 1–400)
Simonsborg (AD 1–200)
Skovgaarde (AD 200–400)
|
24/03
|
12,5%
|
Melchior 2008a, Hofreiter 2010
|
Cemitérios da Era Viking Galgedil (1000 DC)
Cemitério cristão Kongemarken (1000–1250 DC)
cemitério medieval Riisby (1250–1450 DC)
|
29/04
|
13,79%
|
Melchior 2008, Hofreiter 2010
|
Túmulos anglo-saxões
Leicester: 6
Lavington: 6
Buckland: 7
Norton: 12
Norwich: 17
|
1/48
|
2,08%
|
Töpf 2006
|
Observamos anteriormente uma alta frequência de Hg I entre os aldeões da Idade do Ferro (Bøgebjerggård) e indivíduos do cemitério cristão primitivo, Kongemarken [16], [17]. Essa tendência também foi encontrada para os sites adicionais relatados aqui, Simonsborg, Galgedil e Riisby. A frequência geral de Hg I entre os indivíduos da Idade do Ferro à Idade Média é de 13% (7/53) em comparação com 2,5% para os dinamarqueses modernos [35]. As frequências mais altas de Hg I não podem ser atribuídas ao parentesco materno, uma vez que apenas dois indivíduos compartilham o mesmo motivo comum (K2 e K7 em Kongemarken). Exceto para Skovgaarde (nenhum Hg I observado) as frequências variam entre 9% e 29% e parece não haver tendência em relação ao tempo. Nenhum Hg I foi observado no Neolítico Damsbo e no local da Idade do Bronze em Bredtoftegård, onde todos os três indivíduos abrigavam Hg U4 ou Hg U5a (Tabela 1).
Hofreiter 2010
A frequência do haplogrupo I pode ter sofrido uma redução na Europa após a Idade Média. Uma frequência geral de 13% foi encontrada em amostras dinamarquesas antigas da Idade do Ferro à Idade Média (incluindo vikings ) da Dinamarca e da Escandinávia, em comparação com apenas 2,5% nas amostras modernas. Como o haplogrupo I não é observado em nenhum italiano antigo, espanhol [contradito pelas pesquisas recentes que foram encontradas na Itália pré-neolítica, bem como na Espanha neolítica], britânicos, populações da Europa central, primeiros agricultores da Europa central e amostras do Neolítico, de acordo com o autores "Haplogrupo I poderia, portanto, ter sido um tipo antigo do sul da Escandinávia" diluído "por eventos de imigração posteriores" ( Hofreiter 2010 ).
Subclades
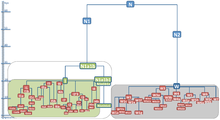
Árvore filogenética dos haplogrupos I (esquerda) e
W (direita). Kya na barra de escala à esquerda representa mil anos atrás (
Olivieri 2013 ).
Árvore
Esta árvore filogenética de subclados do haplogrupo I com estimativas de tempo é baseada no artigo e em pesquisas publicadas ( Olivieri 2013 ).
|
Hg (julho de 2013)
|
Estimativa de idade (mil anos)
|
Intervalo de confiança de 95% (mil anos)
|
| N1a1b |
28,6 |
23,5 - 33,9
|
| eu |
20,1 |
18,4 - 21,9
|
| I1 |
16,3 |
14,6 - 18,0
|
| I1a |
11,6 |
9,9 - 13,3
|
| I1a1 |
4,9 |
4,2 - 5,6
|
| I1a1a |
3,8 |
3,3 - 4,4
|
| I1a1b |
1,4 |
0,5 - 2,2
|
| I1a1c |
2,5 |
1,3 - 3,7
|
| I1a1d |
1,8 |
1,0 - 2,6
|
| I1b |
13,4 |
11,3 - 15,5
|
| I1c |
10,3 |
8,4 - 12,2
|
| I1c1 |
7,2 |
5,4 - 9,0
|
| I1c1a |
4,0 |
2,5 - 5,4
|
| I2'3 |
12,6 |
10,4 - 14,7
|
| I2 |
6,8 |
6,0 - 7,6
|
| I2a |
4,7 |
3,8 - 5,7
|
| I2a1 |
3,2 |
2,1 - 4,4
|
| I2b |
1,7 |
0,5 - 2,9
|
| I2c |
4,7 |
3,6 - 5,8
|
| I2d |
3,0 |
1,1 - 4,8
|
| I2e |
3,1 |
1,4 - 4,8
|
| I3 |
10,6 |
8,8 - 12,4
|
| I3a |
7,4 |
6,1 - 8,7
|
| I3a1 |
6,1 |
4,7 - 7,5
|
| I3b |
2,6 |
1,1 - 4,2
|
| I3c |
9,4 |
7,6 - 11,2
|
| I4 |
15,1 |
12,3 - 18,0
|
| I4a |
6,4 |
5,4 - 7,4
|
| I4a1 |
5,7 |
4,5 - 6,7
|
| I4b |
8,4 |
5,8 - 10,9
|
| I5 |
18,4 |
16,4 - 20,3
|
| I5a |
16,0 |
14,0 - 17,9
|
| I5a1 |
9,2 |
7,1 - 11,3
|
| I5a2 |
12,3 |
10,2 - 14,4
|
| I5a2a |
1,6 |
1.0 - 2.1
|
| I5a3 |
4,8 |
2,8 - 6,8
|
| I5a4 |
5,6 |
3,5 - 7,8
|
| I5b |
8,8 |
6,3 - 11,2
|
| I6 |
18,4 |
16,2 - 20,6
|
| I6a |
5,3 |
3,5 - 7,0
|
| I6b |
13,1 |
10,4 - 15,8
|
| I7 |
9,1 |
6,3 - 11,9
|
Distribuição
I1
| Haplogrupo I1 |
|---|
| Possível hora de origem |
15.231 ± 3.402 BP ( Behar 2012b ) |
| Possível local de origem |
Dados insuficientes |
| Antepassado |
eu |
| Definindo mutações |
455.1T, G6734A, G9966A, T16311C! ( Behar & Family Tree DNA 2012 ) |
Formou-se durante o período de pré-aquecimento do Último Glacial. É encontrada principalmente na Europa, Oriente Médio, ocasionalmente no Norte da África e no Cáucaso. É o clado mais frequente do haplogrupo ( Olivieri 2013 ).
I1a
| Haplogrupo I1a |
|---|
| Possível hora de origem |
11.726 ± 3.306 BP ( Behar 2012b ) |
| Possível local de origem |
Dados insuficientes |
| Antepassado |
I1 |
| Definindo mutações |
T152C !, G207A ( Behar & Family Tree DNA 2012 ) |
Os picos de frequência do subclado (cerca de 2,8%) estão localizados principalmente no Nordeste da Europa ( Olivieri 2013 ).
I1a1
| Haplogrupo I1a1 |
|---|
| Possível hora de origem |
5.294 ± 2.134 BP ( Behar 2012b ) |
| Possível local de origem |
Dados insuficientes |
| Antepassado |
I1a |
| Definindo mutações |
G203A, C3990T, G9947A, A9966G !, T10915C! ( Behar & Family Tree DNA 2012 ) |
I1a1a
I1a1b
| Haplogrupo I1a1b |
|---|
| Possível hora de origem |
2.608 ± 2.973 BP ( Behar 2012b ) |
| Possível local de origem |
Dados insuficientes |
| Antepassado |
I1a1 |
| Definindo mutações |
T14182C ( Behar & Family Tree DNA 2012 ) |
I1a1c
| Haplogrupo I1a1c |
|---|
| Possível hora de origem |
Cerca de 1.523 BP ( Behar 2012b ) |
| Possível local de origem |
Dados insuficientes |
| Antepassado |
I1a1 |
| Definindo mutações |
T6620C ( Behar & Family Tree DNA 2012 ) |
I1a1d
| Haplogrupo I1a1d |
|---|
| Possível hora de origem |
Cerca de 1.892 BP ( Behar 2012b ) |
| Possível local de origem |
Dados insuficientes |
| Antepassado |
I1a1 |
| Definindo mutações |
A1836G, T4023C, T13488C, T16189C! ( Behar & Family Tree DNA 2012 ) |
I1b
I1c
| Haplogrupo I1c |
|---|
| Possível hora de origem |
8.216 ± 3.787 BP ( Behar 2012b ) |
| Possível local de origem |
Dados insuficientes |
| Antepassado |
I1 |
| Definindo mutações |
G8573A, C16264T, G16319A, T16362C ( Behar & Family Tree DNA 2012 ) |
I2'3
| Haplogrupo I2'3 |
|---|
| Possível hora de origem |
11.308 ± 4.154 BP ( Behar 2012b ) |
| Possível local de origem |
Dados insuficientes |
| Antepassado |
eu |
| Definindo mutações |
T152C !, G207A ( Behar & Family Tree DNA 2012 ) |
É o clado raiz comum para os subclados I2 e I3. Há uma amostra da Tanzânia com a qual I2'3 compartilha uma variante na posição 152 do nó raiz do haplogrupo I, e este "nó 152" poderia ser o clado I2'3s a montante ( Olivieri 2013 ). Ambos I2 e I3 podem ter se formado durante o período do Holoceno, e a maioria de seus subclados são da Europa, apenas alguns do Oriente Próximo ( Olivieri 2013 ). Exemplos deste ramo ancestral não foram documentados.
I2
I2a
| Haplogrupo I2a |
|---|
| Possível hora de origem |
3.771 ± 2.143 BP ( Behar 2012b ) |
| Possível local de origem |
Dados insuficientes |
| Antepassado |
I2 |
| Definindo mutações |
A11065G, G16145A ( Behar & Family Tree DNA 2012 ) |
I2a1
I2b
| Haplogrupo I2b |
|---|
| Possível hora de origem |
Cerca de 1.267 BP ( Behar 2012b ) |
| Possível local de origem |
Dados insuficientes |
| Antepassado |
I2 |
| Definindo mutações |
T6515C, 8281-8289d, A16166c ( Behar & Family Tree DNA 2012 ) |
I2c
| Haplogrupo I2c |
|---|
| Possível hora de origem |
Cerca de 2.268 BP ( Behar 2012b ) |
| Possível local de origem |
Dados insuficientes |
| Antepassado |
I2 |
| Definindo mutações |
T460C, G9438A ( Behar & Family Tree DNA 2012 ) |
I2d
I2e
I3
I3a
| Haplogrupo I3a |
|---|
| Possível hora de origem |
6.091 ± 3.262 BP ( Behar 2012b ) |
| Possível local de origem |
Amostra mais antiga da cultura Poltavka (Rússia-Lopatino II, Rio Sok, Samara, 2885-2665 AC) (Mathieson 2015) |
| Antepassado |
I3 |
| Definindo mutações |
T16086C ( Behar & Family Tree DNA 2012 ) |
I3a1
I3b
I4
O clado se divide em subclados I4a e I4b recém-definido, com amostras encontradas na Europa, Oriente Próximo e Cáucaso ( Olivieri 2013 ).
I4a
I5
É o segundo clado mais frequente do haplogrupo. Seus subclados são encontrados na Europa, por exemplo, I5a1, e no Oriente Próximo, por exemplo, I5a2a e I5b ( Olivieri 2013 ).
I5a
| Haplogrupo I5a |
|---|
| Possível hora de origem |
15.116 ± 4.128 BP ( Behar 2012b ) |
| Possível local de origem |
Dados insuficientes |
| Antepassado |
I5 |
| Definindo mutações |
T5074C, C16148T ( Behar & Family Tree DNA 2012 ) |
I5a1
| Haplogrupo I5a1 |
|---|
| Possível hora de origem |
11.062 ± 4.661 BP ( Behar 2012b ) |
| Possível local de origem |
Dados insuficientes |
| Antepassado |
I5a |
| Definindo mutações |
8281-8289d, A12961G ( Behar & Family Tree DNA 2012 ) |
I6
O subclado é muito raro, encontrado até julho de 2013 apenas em quatro amostras do Oriente Próximo ( Olivieri 2013 ).
I6a
| Haplogrupo I6a |
|---|
| Possível hora de origem |
Cerca de 5.300 BP ( Olivieri 2013 ) |
| Possível local de origem |
Dados insuficientes |
| Antepassado |
I6 |
| Definindo mutações |
(G203A), G3915A, A6116G, A7804G, T15287C, (A16293c) ( Behar & Family Tree DNA 2012 ) |
I7
| Haplogrupo I7 |
|---|
| Possível hora de origem |
Cerca de 9.100 BP ( Olivieri 2013 ) |
| Possível local de origem |
Dados insuficientes |
| Antepassado |
eu |
| Definindo mutações |
C3534T, A4829G, T16324C |
É o subclado definido mais raro, até julho de 2013, encontrado apenas em duas amostras do Oriente Próximo e do Cáucaso ( Olivieri 2013 ).
Veja também
Genética
Árvore mtDNA da espinha dorsal
Referências
Trabalhos citados
Diários
-
Behar, DM; Metspalu, E; Kivisild, T; Rosset, S; Tzur, S; Hadid, Y; Yudkovsky, G; Rosengarten, D; et al. (2008). MacAulay, Vincent (ed.). "Contando os fundadores: a ancestralidade genética matrilinear da Diáspora Judaica" . PLOS ONE . 3 (4): e2062. Bibcode : 2008PLoSO ... 3.2062B . doi : 10.1371 / journal.pone.0002062 . PMC 2323359 . PMID 18446216 .
-
Behar, Doron M .; Van Oven, Mannis; Rosset, Saharon; Metspalu, Mait; Loogväli, Eva-Liis; Silva, Nuno M .; Kivisild, Toomas; Torroni, Antonio; Villems, Richard (2012). "Uma reavaliação" copernicana "da árvore do DNA mitocondrial humano a partir de sua raiz" . The American Journal of Human Genetics . 90 (4): 675–84. doi : 10.1016 / j.ajhg.2012.03.002 . PMC 3322232 . PMID 22482806 .
-
Belyaeva, Olga; Bermisheva, Marina; Khrunin, Andrey; Slominsky, Petr; Bebyakova, Natalia; Khusnutdinova, EK (Elza Kamilevna); Mikulich, Aleksei Ignatevich; Limbourskaia, SA (Svetlana Andreevna) (2003). "Variações do DNA mitocondrial em populações russas e bielorrussas". Biologia Humana . 75 (5): 647–60. doi : 10.1353 / hub.2003.0069 . PMID 14763602 . S2CID 23876546 .
-
Boattini, Alessio; Castrì, Loredana; Sarno, Stefania; Useli, Antonella; Cioffi, Manuela; Sazzini, Marco; Garagnani, Paolo; De Fanti, Sara; Pettener, Davide; Luiselli, Donata (2013). "Variação do MtDNA na África Oriental desvenda a história dos grupos afro-asiáticos". American Journal of Physical Anthropology . 150 (3): 375–385. doi : 10.1002 / ajpa.22212 . PMID 23283748 .
-
Bosch, E .; Calafell, F .; Gonzalez-Neira, A .; Flaiz, C .; Mateu, E .; Scheil, H.-G .; Huckenbeck, W .; Efremovska, L .; et al. (2006). "As linhagens paternas e maternas nos Balcãs mostram uma paisagem homogênea sobre as barreiras linguísticas, exceto para os isolados Aromuns". Annals of Human Genetics . 70 (4): 459–87. doi : 10.1111 / j.1469-1809.2005.00251.x . PMID 16759179 . S2CID 23156886 .
-
Brandt, G .; Haak, W .; Adler, C .; Roth, C .; Szécsényi-Nagy, A .; Karimnia, S .; Möller-Rieker, S .; Meller, H .; Ganslmeier, R .; Friederich, S .; Dresely, V .; Nicklisch, N .; Pickrell, J .; Sirocko, F .; Reich, D .; Cooper, A .; Alt, K .; The Genographic Consortium (2013). "O DNA antigo revela estágios-chave na formação da diversidade genética mitocondrial da Europa Central" . Ciência . 342 (6155): 257–261. Bibcode : 2013Sci ... 342..257B . doi : 10.1126 / science.1241844 . PMC 4039305 . PMID 24115443 .
-
Brandstatter, Anita; Peterson, Christine T .; Irwin, Jodi A .; Mpoke, Solomon; Koech, Davy K .; Parson, Walther; Parsons, Thomas J. (2004). "Sequências da região de controle do DNA mitocondrial de Nairobi (Quênia): inferir parâmetros filogenéticos para o estabelecimento de um banco de dados forense". International Journal of Legal Medicine . 118 (5): 294–306. doi : 10.1007 / s00414-004-0466-z . PMID 15248073 . S2CID 19703169 .
-
Castrì, Loredana; Garagnani, P; Useli, A; Pettener, D; Luiselli, D (2008). "Encruzilhada do Quênia: migração e fluxo gênico em seis grupos étnicos da África Oriental". Journal of Anthropological Sciences . 86 : 189–192. PMID 19934476 .
-
Castrì, Loredana; Tofanelli, Sergio; Garagnani, Paolo; Bini, Carla; Fosella, Xenia; Pelotti, Susi; Paoli, Giorgio; Pettener, Davide; Luiselli, Donata (2009). "Variabilidade do MtDNA em duas populações de língua Bantu (Shona e Hutu) da África Oriental: Implicações para o povoamento e os padrões de migração na África Subsaariana". American Journal of Physical Anthropology . 140 (2): 302–11. doi : 10.1002 / ajpa.21070 . PMID 19425093 .
-
Costa, MD; Cherni, L; Fernandes, V; Freitas, F; Ammar El Gaaied, AB; Pereira, L (2009). "Dados do sequenciamento completo do mtDNA de centenários tunisianos: Testando a associação de haplogrupos e a" média de ouro "para a longevidade". Mecanismos de envelhecimento e desenvolvimento . 130 (4): 222–6. doi : 10.1016 / j.mad.2008.12.001 . PMID 19133286 . S2CID 6102820 .
-
Cvjetan, S; Tolk, HV; Lauc, LB; Colak, I; Dordević, D; Efremovska, L; Janićijević, B; Kvesić, A; et al. (2004). "Frequências de haplogrupos mtDNA no sudeste da Europa - croatas, bósnios e herzegovinos, sérvios, macedônios e romani macedônio". Collegium Antropologicum . 28 (1): 193–8. PMID 15636075 .
-
Derenko, M; Malyarchuk, B; Grzybowski, T; Denisova, G; Dambueva, eu; Perkova, M; Dorzhu, C; Luzina, F; et al. (2007). "Análise filogeográfica do DNA mitocondrial em populações do norte da Ásia" . American Journal of Human Genetics . 81 (5): 1025–41. doi : 10.1086 / 522933 . PMC 2265662 . PMID 17924343 .
-
Dubut, Vincent; Chollet, Lionel; Murail, Pascal; Cartault, François; Béraud-Colomb, Eliane; Serre, Myriam; Mogentale-Profizi, Nérina (2003). "Polimorfismos MtDNA em cinco grupos franceses: Importância da amostragem regional" . European Journal of Human Genetics . 12 (4): 293–300. doi : 10.1038 / sj.ejhg.5201145 . PMID 14694359 .
-
Fernandes, Verónica; Alshamali, Farida; Alves, Marco; Costa, Marta D .; Pereira, Joana B .; Silva, Nuno M .; Cherni, Lotfi; Harich, Nourdin; et al. (2012). "O berço árabe: relictos mitocondriais dos primeiros passos ao longo da rota do sul para fora da África" . The American Journal of Human Genetics . 90 (2): 347–355. doi : 10.1016 / j.ajhg.2011.12.010 . PMC 3276663 . PMID 22284828 .
-
Finnila, JS; Finnila, S; Majamaa, K (2001). "Seleção específica de linhagem em mtDNA humano: Falta de polimorfismos em um segmento do gene MTND5 no haplogrupo J" . Biologia Molecular e Evolução . 20 (12): 2132–42. doi : 10.1093 / molbev / msg230 . PMID 12949126 .
-
Gasparre, G .; Porcelli, AM; Bonora, E .; Pennisi, LF; Toller, M .; Iommarini, L .; Ghelli, A .; Moretti, M .; et al. (2007). "Mutações disruptivas do DNA mitocondrial em subunidades do complexo I são marcadores do fenótipo oncocítico em tumores da tireoide" . Proceedings of the National Academy of Sciences . 104 (21): 9001–9006. Bibcode : 2007PNAS..104.9001G . doi : 10.1073 / pnas.0703056104 . PMC 1885617 . PMID 17517629 .
-
Gonder, MK; Mortensen, HM; Reed, FA; De Sousa, A .; Tishkoff, SA (2006). "Whole-mtDNA Genome Sequence Analysis of Ancient African Lineages" . Biologia Molecular e Evolução . 24 (3): 757–68. doi : 10.1093 / molbev / msl209 . PMID 17194802 .
-
Hartmann, A; Thieme, M; Nanduri, LK; Stempfl, T; Moehle, C; Kivisild, T; Oefner, PJ (2009). "Validação de resequenciamento baseado em microarray de 93 genomas mitocondriais em todo o mundo". Mutação Humana . 30 (1): 115–22. doi : 10.1002 / humu.20816 . PMID 18623076 . S2CID 205918494 .
-
Helgason, Agnar; Hickey, Eileen; Goodacre, Sara; Bosnes, Vidar; Stefánsson, Kári; Ward, Ryk; Sykes, Bryan (2001). "mtDNA e as ilhas do Atlântico Norte: estimando as proporções da ancestralidade nórdica e gaélica" . The American Journal of Human Genetics . 68 (3): 206-15. doi : 10.1086 / 318785 . PMC 1274484 . PMID 11179019 .
-
Hofreiter, Linea; Lynnerup, Niels; Siegismund, Hans R .; Kivisild, Toomas; Dissing, Jørgen (2010). Hofreiter, Michael (ed.). "Diversidade genética entre populações nórdicas antigas" . PLOS ONE . 5 (7): e11898. Bibcode : 2010PLoSO ... 511898M . doi : 10.1371 / journal.pone.0011898 . PMC 2912848 . PMID 20689597 .
A ocorrência geral de haplogrupos não se desviou dos escandinavos existentes, no entanto, o haplogrupo I foi significativamente mais frequente entre os dinamarqueses antigos (em média 13%) do que entre os dinamarqueses e escandinavos existentes (~ 2,5%), bem como entre outras amostras populacionais antigas relatadas. O Haplogrupo I poderia, portanto, ter sido um tipo antigo da Escandinávia do Sul “diluído” por eventos posteriores de imigração.
-
Janssen, GM; Neu, A; 't Hart, LM; Van De Sande, CM; Antonie Maassen, J (2006). "Novas variantes de comprimento de DNA mitocondrial e instabilidade genética em uma família com diabetes e surdez". Endocrinologia e Diabetes Experimental e Clínica . 114 (4): 168–74. doi : 10.1055 / s-2006-924066 . PMID 16705548 .
-
Keyser, Christine; Bouakaze, Caroline; Crubézy, Eric; Nikolaev, Valery G .; Montagnon, Daniel; Reis, Tatiana; Ludes, Bertrand (2009). "O DNA antigo fornece novos insights sobre a história do povo Kurgan do sul da Sibéria". Genética Humana . 126 (3): 395–410. doi : 10.1007 / s00439-009-0683-0 . PMID 19449030 . S2CID 21347353 .
-
Kivisild, T; Reidla, M; Metspalu, E; Rosa, A; Brehm, A; Pennarun, E; Parik, J; Geberhiwot, T; et al. (2004). "Herança do DNA mitocondrial etíope: Rastreamento do fluxo gênico através e ao redor do portal das lágrimas" . American Journal of Human Genetics . 75 (5): 752–70. doi : 10.1086 / 425161 . PMC 1182106 . PMID 15457403 .
-
Cavaleiro, A; Underhill, PA; Mortensen, HM; Zhivotovsky, LA; Lin, AA; Henn, BM; Louis, D; Ruhlen, M; Mountain, JL (2003). "A divergência do cromossomo Y africano e do mtDNA fornece uma visão sobre a história das linguagens de clique" . Biologia atual . 13 (6): 464–73. doi : 10.1016 / S0960-9822 (03) 00130-1 . PMID 12646128 . S2CID 52862939 .
-
Krings, M; Salem, AE; Bauer, K; Geisert, H; Malek, AK; Chaix, L; Simon, C; Welsby, D; et al. (1999). "Análise de MtDNA de populações do Vale do Rio Nilo: um corredor genético ou uma barreira para a migração?" . American Journal of Human Genetics . 64 (4): 1166–1176. doi : 10.1086 / 302314 . PMC 1377841 . PMID 10090902 .
-
Lalueza-Fox, C; Sampietro, ML; Gilbert, MT; Castri, L; Facchini, F; Pettener, D; Bertranpetit, J (2004). "Desvendando migrações na estepe: sequências de DNA mitocondrial de antigos asiáticos centrais" . Anais: Ciências Biológicas . 271 (1542): 941–7. doi : 10.1098 / rspb.2004.2698 . PMC 1691686 . PMID 15255049 .
-
Lazaridis, Iosif (2016). "Insights genômicos sobre a origem da agricultura no antigo Oriente Próximo" . Nature . 536 (7617): 419–24. Bibcode : 2016Natur.536..419L . doi : 10.1038 / nature19310 . PMC 5003663 . PMID 27459054 .
-
Maca-Meyer, N; González, AM; Larruga, JM; Flores, C; Cabrera, VM (2001). "As principais linhagens mitocondriais genômicas delineiam as primeiras expansões humanas" . BMC Genetics . 2 : 13. doi : 10.1186 / 1471-2156-2-13 . PMC 55343 . PMID 11553319 .
-
MacAulay, Vincent; Richards, Martin; Hickey, Eileen; Vega, Emilce; Cruciani, Fulvio; Guida, Valentina; Scozzari, Rosaria; Bonné-Tamir, Batsheva; et al. (1999). "The Emerging Tree of West Eurasian mtDNAs: A Synthesis of Control-Region Sequences and RFLPs" . The American Journal of Human Genetics . 64 (1): 232–49. doi : 10.1086 / 302204 . PMC 1377722 . PMID 9915963 .
-
Malyarchuk, BA; Derenko, MV (2001). "Variabilidade do DNA mitocondrial em russos e ucranianos: implicação na origem dos eslavos orientais" . Annals of Human Genetics . 65 (Pt 1): 63–78. doi : 10.1046 / j.1469-1809.2001.6510063.x . PMID 11415523 . S2CID 9392520 .
-
Malyarchuk, BA; Grzybowski, T; Derenko, MV; Czarny, J; Drobnic, K; Miścicka-Sliwka, D (2003). "Variabilidade do DNA mitocondrial em bósnios e eslovenos". Annals of Human Genetics . 67 (Pt 5): 412–25. doi : 10.1046 / j.1469-1809.2003.00042.x . PMID 12940915 . S2CID 2105448 .
-
Malyarchuk, B; Derenko, M; Denisova, G; Kravtsova, O (2010). "Diversidade mitogenômica em tártaros da região do Volga-Ural da Rússia" . Biologia Molecular e Evolução . 27 (10): 2220–6. doi : 10.1093 / molbev / msq065 . PMID 20457583 .
-
Martinez-Cruz, B .; Harmant, C .; Platt, DE; Haak, W .; Manry, J .; Ramos-Luis, E .; Soria-Hernanz, DF; Bauduer, F .; et al. (2012). "Evidência da estrutura genética tribal pré-romana em bascos a partir de marcadores herdados uniparentalmente" (PDF) . Biologia Molecular e Evolução . 29 (9): 2211–22. doi : 10.1093 / molbev / mss091 . PMID 22411853 .
-
Melchior, Linea; Kivisild, Toomas; Lynnerup, Niels; Dissing, Jørgen (2008). Ahmed, Niyaz (ed.). "Evidência de DNA autêntico de esqueletos da era Viking dinamarquês intocados por humanos por 1.000 anos" . PLOS ONE . 3 (5): e2214. Bibcode : 2008PLoSO ... 3.2214M . doi : 10.1371 / journal.pone.0002214 . PMC 2386972 . PMID 18509537 .
-
Metspalu, Mait; Kivisild, Toomas; Metspalu, Ene; Parik, Jüri; Hudjashov, Georgi; Kaldma, Katrin; Serk, Piia; Karmin, Monika; Behar, Doron M; Gilbert, M. Thomas P; Endicott, Phillip; Mastana, Sarabjit; Papiha, Surinder S; Skorecki, Karl; Torroni, Antonio; Villems, Richard (2004). "A maioria das fronteiras do mtDNA existentes no sul e sudoeste da Ásia foram provavelmente moldadas durante a colonização inicial da Eurásia por humanos anatomicamente modernos" . BMC Genetics . 5 : 26. doi : 10.1186 / 1471-2156-5-26 . PMC 516768 . PMID 15339343 .
-
Mikkelsen, Martin; Sørensen, Erik; Rasmussen, Erik Michael; Morling, Niels (2010). "Variação do DNA mitocondrial HV1 e HV2 em dinamarqueses". Ciência Forense Internacional: Genética . 4 (4): e87-8. doi : 10.1016 / j.fsigen.2009.07.007 . PMID 20457038 .
-
Mishmar, D; Ruiz-Pesini, E; Golik, P; MacAulay, V; Clark, AG; Hosseini, S; Brandon, M; Easley, K; et al. (2003). "A seleção natural moldou a variação regional do mtDNA em humanos" . Anais da Academia Nacional de Ciências dos Estados Unidos da América . 100 (1): 171–6. Bibcode : 2003PNAS..100..171M . doi : 10.1073 / pnas.0136972100 . PMC 140917 . PMID 12509511 .
-
Modi, Alessandra (2017). "Sequências mitocondriais completas do Mesolítico da Sardenha" . Relatórios científicos . 7 : 42869. bibcode : 2017NatSR ... 742869M . doi : 10.1038 / srep42869 . PMC 5335606 . PMID 28256601 .
-
Musilová, Eliška; Fernandes, Verónica; Silva, Nuno M .; Soares, Pedro; Alshamali, Farida; Harich, Nourdin; Cherni, Lotfi; Gaaied, Amel Ben Ammar El; et al. (2011). "História da população das trocas genéticas do Mar Vermelho entre a Península Arábica e a África Oriental sinalizada no haplogrupo HV1 do DNA mitocondrial". American Journal of Physical Anthropology . 145 (4): 592–8. doi : 10.1002 / ajpa.21522 . PMID 21660931 .
-
Nikitin, Alexey G .; Kochkin, Igor T .; Junho, Cynthia M .; Willis, Catherine M .; McBain, Ian; Videiko, Mykhailo Y. (2009). "Variação da sequência de DNA mitocondrial nas populações Boyko, Hutsul e Lemko das Terras Altas dos Cárpatos". Biologia Humana . 81 (1): 43–58. doi : 10.3378 / 027.081.0104 . PMID 19589018 . S2CID 45791162 .
-
Non, Amy L .; Al-Meeri, Ali; Raaum, Ryan L .; Sanchez, Luisa F .; Mulligan, Connie J. (2011). "O DNA mitocondrial revela histórias evolutivas distintas para as populações judaicas no Iêmen e na Etiópia". American Journal of Physical Anthropology . 144 (1): 1–10. doi : 10.1002 / ajpa.21360 . PMID 20623605 .
-
Olivieri, Anna; Pala, Maria; Gandini, Francesca; Kashani, Baharak Hooshiar; Perego, Ugo A .; Woodward, Scott R .; Grugni, Viola; Battaglia, Vincenza; Semino, Ornella; Achilli, Alessandro; Richards, Martin B .; Torroni, Antonio (2013). "Mitogenomes from Two Uncommon Haplogroups Mark Late Glacial / Postglacial Expansions from the Near East e Neolithic Dispersals dentro da Europa" . PLOS ONE . 8 (7): e70492. Bibcode : 2013PLoSO ... 870492O . doi : 10.1371 / journal.pone.0070492 . PMC 3729697 . PMID 23936216 .
-
Palanichamy, MG; Sun, C; Agrawal, S; Bandelt, HJ; Kong, QP; Khan, F; Wang, CY; Chaudhuri, TK; et al. (2004). "Filogenia do macrohaplogrupo N do DNA mitocondrial na Índia, com base no sequenciamento completo: implicações para o povoamento do sul da Ásia" . American Journal of Human Genetics . 75 (6): 966–78. doi : 10.1086 / 425871 . PMC 1182158 . PMID 15467980 .
-
Pereira, L; Gonçalves, J; Franco-Duarte, R; Silva, J; Rocha, T; Arnold, C; Richards, M; MacAulay, V (2007). "Nenhuma evidência de um papel do mtDNA na motilidade do esperma: dados do sequenciamento completo de homens astenozoospérmicos" . Biologia Molecular e Evolução . 24 (3): 868–74. doi : 10.1093 / molbev / msm004 . PMID 17218641 .
-
Pericić, M; Barać Lauc, L; Martinović Klarić, I; Janićijević, B; Rudan, P (2005). "Revisão da herança genética croata revelada pelo DNA mitocondrial e linhagens cromossômicas Y". Croatian Medical Journal . 46 (4): 502–13. PMID 16100752 .
-
Pichler, Irene; Fuchsberger, cristão; Platzer, Christa; Çalişkan, Minal; Marroni, Fabio; Pramstaller, Peter P; Ober, Carole (2010). "Desenhando a história da população huterita em uma paisagem genética: inferência do cromossomo Y e genótipos do mtDNA" . European Journal of Human Genetics . 18 (4): 463–70. doi : 10.1038 / ejhg.2009.172 . PMC 2987252 . PMID 19844259 .
-
Poloni, Estella S .; Naciri, Yamama; Bucho, Rute; Niba, Régine; Kervaire, Barbara; Excoffier, Laurent; Langaney, André; Sanchez-Mazas, Alicia (2009). "Evidência genética para complexidade na diferenciação étnica e história na África Oriental" . Annals of Human Genetics . 73 (6): 582–600. doi : 10.1111 / j.1469-1809.2009.00541.x . PMID 19706029 . S2CID 2488794 .
-
Pope, AM; Carr, SM; Smith, KN; Marshall, HD; Marshall, HD (2011). "Variação mitogenômica e microssatélites em descendentes da população fundadora de Terra Nova: Alta diversidade genética em uma população historicamente isolada". Genoma . 54 (2): 110–9. doi : 10.1139 / G10-102 . PMID 21326367 .
-
Quintana-Murci, Lluís; Chaix, Raphaëlle; Wells, R. Spencer; Behar, Doron M .; Sayar, Hamid; Scozzari, Rosaria; Rengo, Chiara; Al-Zahery, Nadia; et al. (2004). "Onde o oeste encontra o leste: a paisagem complexa do mtDNA do corredor da Ásia Central e do sudoeste" . The American Journal of Human Genetics . 74 (5): 827–45. doi : 10.1086 / 383236 . PMC 1181978 . PMID 15077202 .
-
Richards, Martin; MacAulay, Vincent; Hickey, Eileen; Vega, Emilce; Sykes, Bryan; Guida, Valentina; Rengo, Chiara; Sellitto, Daniele; et al. (2000). "Traçando Linhagens Fundadoras Européias no Conjunto de mtDNA do Oriente Próximo" . The American Journal of Human Genetics . 67 (5): 1251–76. doi : 10.1016 / S0002-9297 (07) 62954-1 . PMC 1288566 . PMID 11032788 .
-
Richards, Martin; Rengo, Chiara; Cruciani, Fulvio; Gratrix, Fiona; Wilson, James F .; Scozzari, Rosaria; MacAulay, Vincent; Torroni, Antonio (2003). "Extensivo fluxo gênico mediado por mulheres da África Subsaariana para as populações árabes do Oriente Próximo" . The American Journal of Human Genetics . 72 (4): 1058–64. doi : 10.1086 / 374384 . PMC 1180338 . PMID 12629598 .
-
Shlush, Liran I .; Behar, Doron M .; Yudkovsky, Guennady; Templeton, Alan; Hadid, Yarin; Basis, Fuad; Martelo, Michael; Itzkovitz, Shalev; Skorecki, Karl (2008). Gemmell, Neil John (ed.). "O Druze: A Population Genetic Refugium of the Near East" . PLOS ONE . 3 (5): e2105. Bibcode : 2008PLoSO ... 3.2105S . doi : 10.1371 / journal.pone.0002105 . PMC 2324201 . PMID 18461126 .
-
Soares, P .; Alshamali, F .; Pereira, JB; Fernandes, V .; Silva, NM; Afonso, C .; Costa, MD; Musilova, E .; et al. (2011). "A expansão do haplogrupo L3 do mtDNA dentro e fora da África" . Biologia Molecular e Evolução . 29 (3): 915–27. doi : 10.1093 / molbev / msr245 . PMID 22096215 .
-
Stevanovitch, A .; Gilles, A .; Bouzaid, R. Kefi; F. Paris, RP; Gayraud, JL; Spadoni, F .; El-Chenawi, E .; Béraud-Colomb (janeiro de 2004). "Diversidade da sequência de DNA mitocondrial em uma população sedentária do Egito". Annals of Human Genetics . 68 (1): 23–39. doi : 10.1046 / j.1529-8817.2003.00057.x . PMID 14748828 . S2CID 44901197 .
-
Terreros, Maria C; Rowold, Diane J; Mirabal, Sheyla; Herrera, Rene J (2011). "DNA mitocondrial e estratificação do cromossomo Y no Irã: a relação entre o Irã e a Península Arábica" . Journal of Human Genetics . 56 (3): 235–46. doi : 10.1038 / jhg.2010.174 . PMID 21326310 .
-
Tishkoff, SA; Gonder, MK; Henn, BM; Mortensen, H .; Knight, A .; Gignoux, C .; Fernandopulle, N .; Lema, G .; et al. (2007). "História das populações que falam cliques da África inferida da variação genética do mtDNA e do cromossomo Y" . Biologia Molecular e Evolução . 24 (10): 2180–95. doi : 10.1093 / molbev / msm155 . PMID 17656633 .
-
Topf, AL; Gilbert, MT; Dumbacher, JP; Hoelzel, AR (2005). "Traçando a Filogeografia das Populações Humanas na Grã-Bretanha com base nos Genótipos do mtDNA do século 4 ao 11" . Biologia Molecular e Evolução . 23 (1): 152–61. doi : 10.1093 / molbev / msj013 . PMID 16151183 .
-
Torroni, A; Huoponen, K; Francalacci, P; Petrozzi, M; Morelli, L; Scozzari, R; Obinu, D; Savontaus, ML; Wallace, DC (1996). "Classificação de mtDNAs europeus de uma análise de três populações europeias" . Genética . 144 (4): 1835–50. doi : 10.1093 / genetics / 144.4.1835 . PMC 1207732 . PMID 8978068 .
-
van Oven, Mannis; Kayser, Manfred (2009). "Árvore filogenética abrangente atualizada da variação global do DNA mitocondrial humano" . Mutação Humana . 30 (2): E386–94. doi : 10.1002 / humu.20921 . PMID 18853457 . S2CID 27566749 .
Sites
Leitura adicional
-
Černý, Viktor; Pereira, Luísa; Kujanová, Martina; VašÍková, Alžběta; Hájek, Martin; Morris, Miranda; Mulligan, Connie J. (2009). "Fora da Arábia-O povoamento da Ilha Soqotra conforme revelado pela diversidade genética mitocondrial e do cromossomo Y". American Journal of Physical Anthropology . 138 (4): 439–47. doi : 10.1002 / ajpa.20960 . PMID 19012329 .
-
Fellner, Robert O (1995). Mudança cultural e o epipalaeolítico da Palestina . Tempus Reparatum. ISBN 9780860547754.
-
Cozinha, A .; Ehret, C .; Assefa, S .; Mulligan, CJ (2009). "A análise filogenética bayesiana das línguas semíticas identifica uma origem do semítico na Idade do Bronze no Oriente Próximo" . Proceedings of the Royal Society B: Biological Sciences . 276 (1668): 2703–10. doi : 10.1098 / rspb.2009.0408 . PMC 2839953 . PMID 19403539 .
-
Petit-Maire, Nicole; Bouysse, Philippe (2000). "Registros geológicos do passado recente, uma chave para os ambientes do mundo futuro próximo" (PDF) . Episódios . 23 (4): 230–246. doi : 10.18814 / epiiugs / 2000 / v23i4 / 001 .
links externos


